Moleküle im Fokus
20.12.2022Eine Software, die bessere Bilder von den Vorgängen innerhalb menschlicher Zellen liefert: Das ist das Ziel eines Forschungsprojekts an der Uni Würzburg. Die Chan Zuckerberg Science Initiative unterstützt das Projekt.
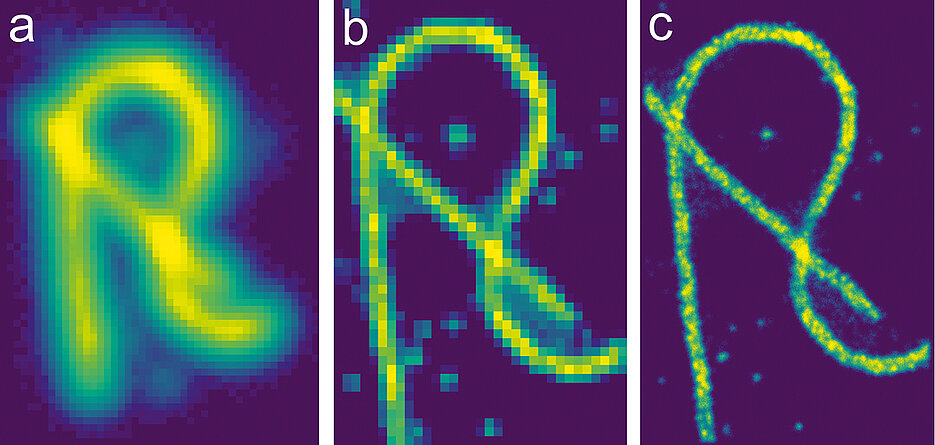
Bildgebende Technologien sind von zentraler Bedeutung, wenn es darum geht, die Grundlagenforschung in praktisch allen Disziplinen der Lebenswissenschaften voranzutreiben. Dabei gilt: Je höher die Auflösung dieser Bilder ist, je kleiner die dargestellten Objekte sind, desto größer ist auch der Erkenntnisgewinn.
Jetzt arbeitet eine Forschungsgruppe am Lehrstuhl für Biotechnologie und Biophysik der Julius-Maximilians-Universität Würzburg (JMU) an der Entwicklung einer neuen Software, mit der es möglich ist, Bilder mit einer extrem hohen Auflösung leichter darzustellen und zu analysieren.
Eine Plattform für die Software-Entwicklung
Verantwortlich für dieses Projekt ist Dr. Sören Doose, Forschungsgruppenleiter am Lehrstuhl für Biotechnologie und Biophysik. Die Chan Zuckerberg Initiative (CZI), eine Stiftung von Facebook-Gründer Mark Zuckerberg und seiner Ehefrau Priscilla Chan, unterstützt das Vorhaben mit 25.000 US-Dollar. Doose kann damit eine lokale Plattform für Software-Entwicklung, -Tests und -Backups innerhalb der Abteilung aufbauen.
„Wenn wir hochauflösende Fluoreszenz-Mikroskopie-Aufnahmen beispielsweise von einzelnen Molekülen machen wollen, setzten wir eine spezielle Technik ein – die sogenannt Einzelmolekül-Lokalisationsmikroskopie, kurz SMLM“, erklärt Doose. Im Unterschied zu klassischen, bildbasierten Mikroskopie-Techniken liefert SMLM punktbasierte Daten, die erst mit speziellen Methoden umgewandelt werden müssen, bevor ein Bild sichtbar wird.
Ein multidimensionaler Bildbetrachter
„Am Lehrstuhl für Biotechnologie und Biophysik verwenden wir solche speziellen Analysewerkzeuge, wenn wir beispielsweise Aufnahmen aus der Fluoreszenzmikroskopie anzeigen und analysieren wollen“, erklärt Doose. Zum Einsatz kommt dabei in der Regel ein sogenannter multidimensionaler Bildbetrachter – eine Software, die auf Basis der Programmiersprache Python entwickelt wurde. Ihr Name lautet Napari.
Napari allein reicht den Wissenschaftlern allerdings noch nicht aus. „Die Vielfalt der kommerziellen und maßgeschneiderten SMLM-Plattformen erfordert ein Napari-Plugin, das die verschiedenen punktförmigen Datenformate liest und verarbeitet“, erklärt Doose. Nur mit Hilfe solcher Plugins ist es möglich, ein zwei- oder dreidimensionales Bild zu erhalten, das in Napari angezeigt und weiterverarbeitet werden kann.
Open-source für alle Mikroskopie-Anwender
Doose und sein Team haben bereits ein Softwarepaket für die SMLM-Datenanalyse entwickelt, das aus einer Python-basierten Bibliothek besteht. Das Napari-Plugin baut auf dieses Paket auf. Dank der finanziellen Unterstützung der Chan Zuckerberg Initiative kann das Team nun die Software weiter den eigenen Anforderungen anpassen, testen und für den Betrieb in der Praxis fit machen. „Unsere Entwicklung wird pixelbasierte Bilder liefern, die für die weitere digitale Bildverarbeitung mit anderen Napari-Plugins leicht verfügbar sind“, verspricht Doose.
Vom Nutzen dieser Entwicklung ist auch Professor Markus Sauer überzeugt, Leiter des Lehrstuhls für Biotechnologie und Biophysik der JMU. „Aus der Erfahrung in meinem Labor kann ich sagen, dass Open-Source-Software wie die Napari-Umgebung allen Mikroskopie-Anwendern, die mit maßgeschneiderten Instrumenten arbeiten, große Vorteile bringt“, sagt er. Eine erfolgreiche Implementierung des neuen Napari-Plugins wird seiner Meinung nach der gesamten Superresolution-Mikroskopie-Gemeinschaft fehlende Funktionalität bieten.
Blick auf einzelne Moleküle und Proteine
Methoden der Superresolution-Mikroskopie bilden einen Schwerpunkt der Forschung am Lehrstuhl für Biotechnologie und Biophysik der JMU. Angewandt auf biologische Proben liefern sie neue Einblicke in die strukturelle Organisation von Zellen und die Dynamik biomolekularer Prozesse. Der hochauflösenden Fluoreszenzmikroskopie kommt dabei eine besondere Rolle zu: Sie ermöglicht den Blick auf einzelne Moleküle sowie Visualisierung der räumlichen Verteilung oder der Anzahl bestimmter Proteine in diversen Zellstrukturen.
Mit Hilfe dieser Technik untersuchen die Wissenschaftlerinnen und Wissenschaftler beispielsweise Rezeptoren auf Tumorzellen und liefern damit wichtige Informationen für eine Krebstherapie mit Immunzellen. In den Neurowissenschaften tragen sie zu einem besseren Verständnis der Vorgänge im menschlichen Gehirn bei, indem sie neue Einblicke in die Signalübertragung an den Synapsen ermöglichen. Alles in allem zeigen sie mit ihrer Arbeit, wie die Natur Funktionen des Lebens auf molekularer Ebene koordiniert.
Kontakt
PD Dr. Sören Doose, Lehrstuhl für Biotechnologie und Biophysik, T: +49 931 31-88734, soeren.doose@uni-wuerzburg.de